解释16SrRNA基因测序结果以评估海洋生态系统健康状况的步骤
1.数据质量控制首先,对测序得到的原始序列数据进行质量控制,去除低质量序列和杂质,确保后续分析的准确性。
2.OTU聚类使用生物信息学软件将相似序列聚类成操作分类单元(OTUs),OTUs通常被用作微生物物种的代理。
3.物种注释将OTUs与已知的16SrRNA基因序列数据库进行比对,以确定每个OTU的可能分类归属,如何解释基因测序结果,以评估海洋生态系统的健康状况这有助于识别海洋生态系统中的微生物种类。
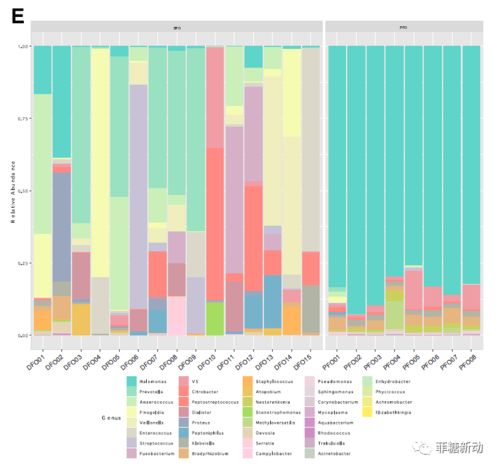
4.群落结构分析分析不同样本中微生物的相对丰度,构建群落结构图,这有助于了解微生物群落的组成和多样性。
5.α多样性和β多样性分析α多样性分析评估单一样本内部的多样性,而β多样性分析评估不同样本之间的多样性差异,这有助于了解海洋生态系统中微生物多样性的空间分布和变化趋势。
6.环境因素相关性分析统计样本的环境参数,并分析这些参数与微生物群落结构之间的相关性,以评估环境因素对微生物群落的影响。
7.健康状态评估综合以上分析结果,评估海洋生态系统的健康状况。健康的海洋生态系统通常具有较高的微生物多样性和稳定的群落结构。如果测序结果显示多样性降低或特定有害微生物的增多,可能表明生态系统受到了污染或其他压力的影响。
8.结果解释根据微生物群落的变化和环境因素的分析,解释海洋生态系统可能面临的问题,并提出相应的管理或保护建议。
在解释16SrRNA基因测序结果时,应特别注意数据的代表性和分析方法的选择,因为这些因素会直接影响到对海洋生态系统健康状况的评估。同时,应关注最新的研究成果和分析技术,以确保评估的准确性和时效性。
【隆科生物合作项目】1.病理检测:石蜡包埋、切片、HE染色、masson染色、番红固绿染色、天狼星红染色、免疫组化、免疫荧光单标/双标/多标、全景扫描、激光共聚焦拍照等。
2.分子生物学实验:荧光定量PCR检测、Westernblot检测、血常规、生化酶活、ELISA检测等。
3.细胞实验:耐药细胞株构建、细胞毒性实验、细胞迁移实验、细胞侵袭实验、细胞流式周期检测、细胞流式凋亡检测等。
4.动物实验:动物模型构建、动物饲养服务、动物临床前研究、药效评价、功能性评价、动物影像学、动物行为学实验等。
5.微生物学实验:抑菌试验、药敏试验、菌种鉴定、微生物多态性分析等实验。











